|
|
 |
| Summary |
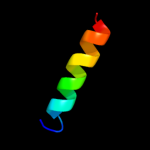
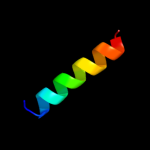
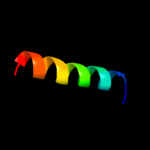
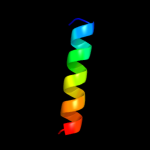
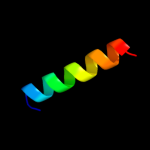
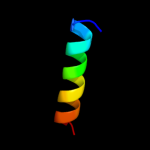
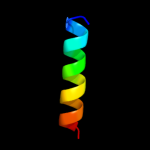
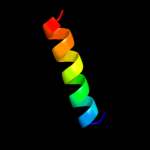
| Top model | |||||||||||||||||
| |||||||||||||||||
| Sequence analysis |
| Secondary structure and disorder prediction |
| 1 | . | . | . | . | . | . | . | . | 10 | . | . | . | . | . | . | . | . | . | 20 | . | . | . | . | . | . | . | . | . | 30 | . | . | . | . | . | . | . | . | . | 40 | . | . | . | . | . | . | . | . | . | 50 | . | . | |||||||||||||||||||||||||||||
| Sequence | M | K | L | P | R | S | S | L | V | W | C | V | L | I | V | C | L | T | L | L | I | F | T | Y | L | T | R | K | S | L | C | E | I | R | Y | R | D | G | Y | R | E | V | A | A | F | M | A | Y | E | S | G | K | ||||||||||||||||||||||||||||
| Secondary structure |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  |  | ||||||||||||||||||||||||||||||||||||||||
| SS confidence | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Disorder | ? | ? | ? | ? | ? | ? | ? | ? | ? | ? | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Disorder confidence | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Confidence Key | |||||||||||
| High(9) | Low (0) | ||||||||||
| ? | Disordered |
  | Alpha helix |
  | Beta strand |
| Domain analysis |
Hover over an aligned region to see model and summary info
Please note, only up to the top 20 hits are modelled to reduce computer load
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|
| Detailed template information |
| Binding site prediction |
Due to computational demand, binding site predictions are not run for batch jobs
If you want to predict binding sites, please manually submit your model of choice to 3DLigandSite
| Transmembrane helix prediction |
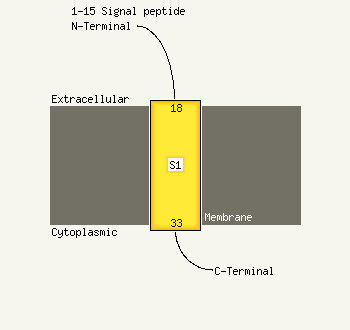
Transmembrane helices have been predicted in your sequence to adopt the topology shown below
Phyre is for academic use only
| Please cite: Protein structure prediction on the web: a case study using the Phyre server | ||||||||||||||
| Kelley LA and Sternberg MJE. Nature Protocols 4, 363 - 371 (2009) [pdf] [Import into BibTeX] | ||||||||||||||
| If you use the binding site predictions from 3DLigandSite, please also cite: | ||||||||||||||
| 3DLigandSite: predicting ligand-binding sites using similar structures. | ||||||||||||||
| Wass MN, Kelley LA and Sternberg MJ Nucleic Acids Research 38, W469-73 (2010) [PubMed] | ||||||||||||||
|
|
| ||||||||||||